一、实验目的、内容与原理
1、实验目的
通过实验教学,使学生学会利用计算机网络系统和国际机构网站的免费资源,分析实验研究获得的DNA序列的相似性,学会构建系统发育树。
2、实验内容与原理
运用NCBI(美国国家生物技术信息中心)的两序列比对分析软件(BLAST)分析两个DNA序列的相似性程度;运用NCBI的核苷酸比对分析软件(nucleotide blast)分析待测DNA序列与国际基因数据库中已有核苷酸序列的相似性程度;运用运用MEGA软件构建系统发育树。
二、仪器、设备与实验材料
计算机、国际互联网、投影仪,DNA序列
三、实验步骤与方法
(一) DNA序列比对分析
一)两个DNA序列的相似性比对分析
1.进入NCBI主页(www.ncbi.nlm.nih.gov)
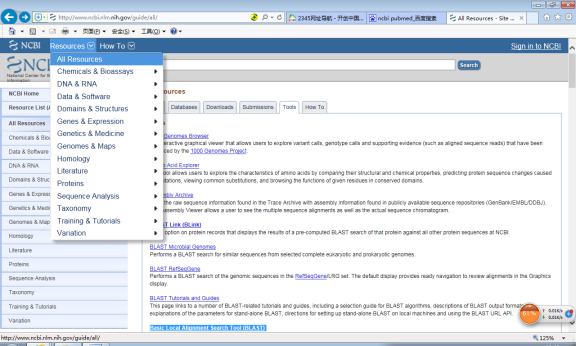
2. 点击所有资源(All Resources)
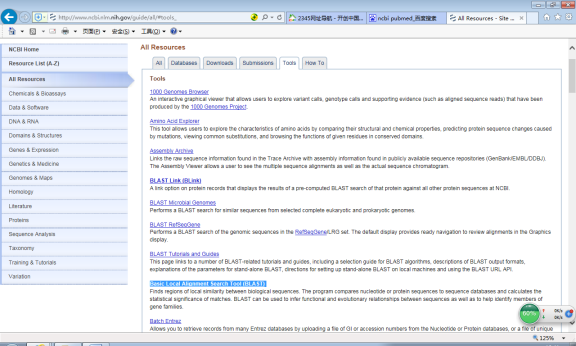
3.点击工具栏目(Tool)
4.在工具栏目里找到Basic Local Alignment Search Tool (BLAST)
点击进入。
- 找到Specialized BLAST,点击Align two (or more) sequences using BLAST (bl2seq)
6. 将序列1复制、黏贴到 Enter Query Sequence框中。
7. 将序列2复制、黏贴到Enter Subject Sequence框中。
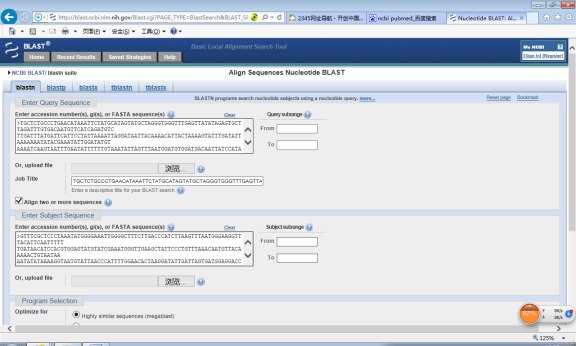
8. 在Program Selection下面,选择Highly similar sequences (megablast) (高度相似序列)或其他分析程序
9、点击BLAST按钮,进行比对分析。
10、观察、记录和分析两序列比对结果。
二)待查DNA序列与国际基因数据库中已有DNA序列的相似性比对分析。
1、进入NCBI主页(www.ncbi.nlm.nih.gov)
2、点击所有资源(all resources)
3.点击工具栏目(Tool)
4.在工具栏目里找到Basic Local Alignment Search Tool (BLAST)
点击进入。
5.在Basic BLAST下,找到nucleotide blast(Search a nucleotide database using a nucleotide query),点击进入。
6. 将DNA序列复制、粘贴到Query Sequence下面的方框中。
7. 在Choose Search Set栏目下,选择others数据库
8. 选择Highly similar sequences (megablast)或其他程序。
9. 按BLAST按钮。
10. 观察、记录和分析DNA序列与国际基因库已有序列的比对结果。
(二)利用MEGA软件构建系统发育树
软件下载:MEGA 5(http://www.megasoftware.net/index.php);DNAMAN 7
1. 准备序列文件
TXT文件中至少选10个序列,分别在GENBANK中用选中的序列做BLAST分析,将其与比对上的最相似序列,拷贝下来构建到一个WORD文件中,同时搜索一个相近物种的同类序列做为系统发育树的外围序列,构建成序列文件:准备fasta格式序列文件(fasta格式:大于号>后紧跟序列名,换行后是序列。举例如下)。每条序列可以单独为一个文件,也可以把所有序列放在同一文件内。
核酸序列:
>sequence1_name
CCTGGCTCAGGATGAACGCT
氨基酸序列:
>sequence2_name
MQSPINSFKKALAEGRTQIGF
2. 多序列比对
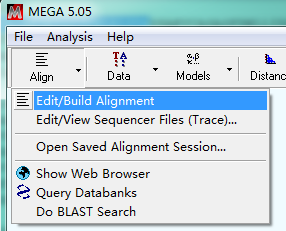
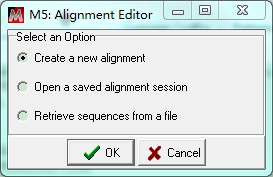
打开MEGA 5,点击Align,选择Edit/Build Alignment,选择Create a new alignment,点击OK。
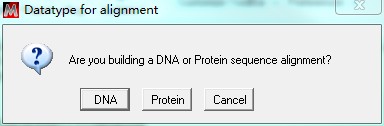
这时需要选择序列类型,核酸(DNA)或氨基酸(Protein)。
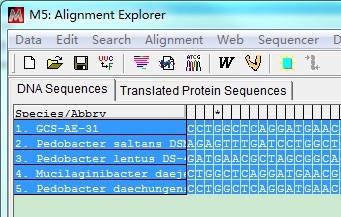
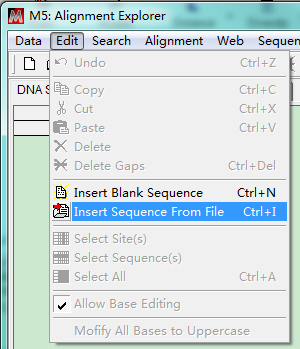
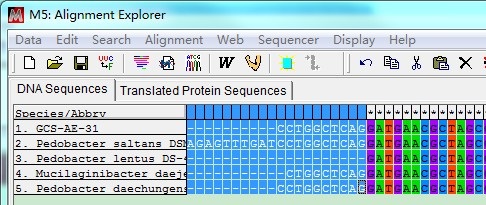
选择之后,在弹出的窗口中直接Ctrl + V粘贴序列(如果所有序列在同一个文件中,即可全选序列,复制)。也可以:点击Edit,选择Insert Sequence From File,选择序列文件(可多选)。
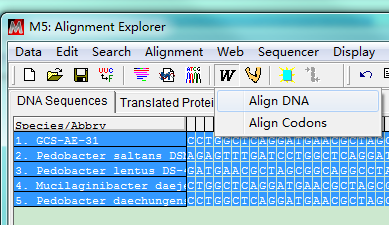
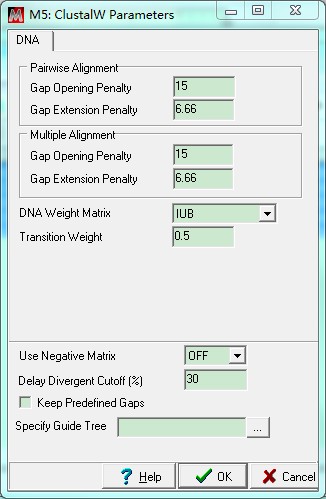
序列文件加载之后,呈蓝色背景(为选中状态)。点击按钮 ,选择Align DNA(如果是氨基酸序列,则会出现Align Protein)。弹出的窗口中设置比对参数,一般都是采用默认参数即可。点击OK,开始多序列比对。
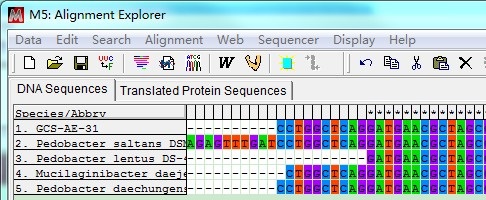
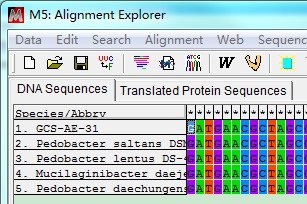
比对完成后,呈现以下状态。
这时需要截齐两端含有---的序列:选中含有---的序列,按键Delete删除(注意:两端都需要截齐)。截齐之后,保存文件为:filename.mas
↓
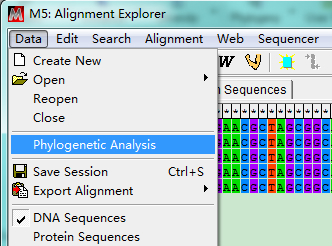
3.构建系统进化树
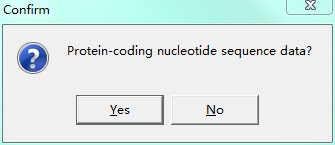
多序列比对窗口,点击Data,选择Phylogenetic Analysis,弹出窗口询问:所用序列是否编码蛋白质,根据实际情况选择Yes或No。此时,多序列比对文件就激活了,可以返回MEGA 5主界面建树了。
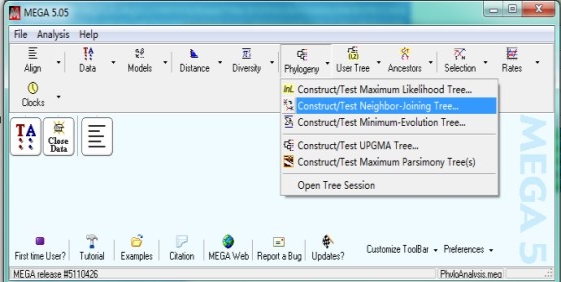
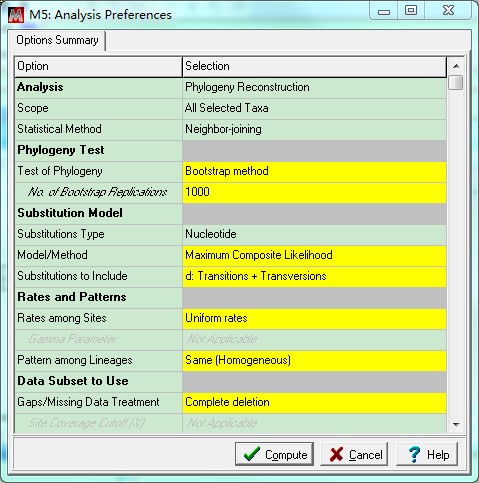
MEGA 5主界面。点击Phylogeny,选择Construct/Test Neighbor-Joining Tree…弹出的对话框询问:是否使用当前激活的数据,选择Yes。这时弹出建树参数设置对话框,更改No. of Bootstrap Replications为1000,其他参数默认即可,点击Compute。
这里解释一下,Construct/Test Maximum Likelihood Tree…(ML)或Construct/Test Neighbor-Joining Tree…(NJ)或Construct/Test Minimum-Evolution Tree…(ME)为三种不同的建树方法,NJ方法最常用。(请选用两种方法分别建树,观察其差别)
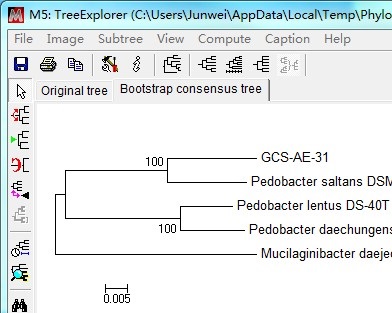
建树完成,效果如下所示。注意,要点击Bootstrap consensus tree查看树形。保存文件为filename.mts(可以用MEGA 5打开)。
4.后期修改
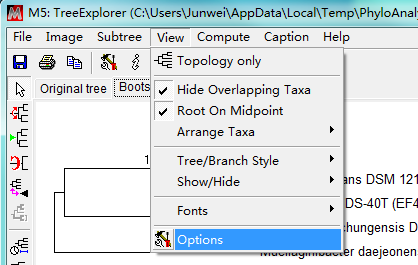
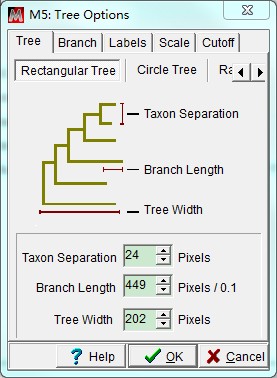
为了美观,也是为了满足发表文章的要求,需要对进化树进行树形、字体、字号的修改。点击View,选择Options。弹出窗口中,在Tree标签中可以修改枝与枝之间的距离(Taxon Separation)、枝长(Branch Length)和树宽(Tree Width),调整至美观即可。Branch标签中,可以选择勾选“Hide values lower than %”,一般隐藏50%以下的数值。其他的参数可以自行研究,一般默认即可。
文字字体、字号的修改。
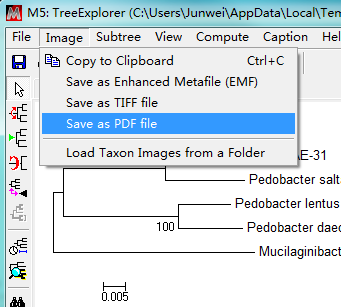
方法1:点击Image,选择Save as PDF file,保存至filename.pdf。打开软件Adobe Illustrator CS6,文件---打开---选择刚刚保存的PDF文件。修改好之后,文件---导出---可以导出很多种类型的文件。一般选择保存成TIFF(.tif)文件,颜色模式选择RGB,勾选LZW压缩,其他默认。
方法2:点击Image,选择Copy to Clipboard。粘贴到Word中,右击进化树图片,编辑图片。即可更改字体字号。修改好可以了。或者进一步导出图片格式:先将该word文件打印生成PDF文件,再用Adobe Illustrator CS6或Adobe Photoshop CS6导出图片格式。
【作业】
提交一个有根树的PDF文件,其中序列数不低于10条,要求有外围,序列名称为物种名加GENEBANK登录号。